Introduction
Insekten spielen eine wichtige Rolle bei der Übertragung von ernährungsbedingter Erkrankungen, da sie Krankheitserreger, um Lebensmittel oder Lebensmittelkontaktflächen und Geschirr 1 ausbreiten. Unter Insekten, Fliegen, Schaben und Ameisen zeigen Verhaltensweisen, die die Verbreitung von Krankheitserregern begünstigen. Diese Verhaltensweisen sind eine Vereinigung mit verfallende Angelegenheit, Abfall und Fäkalien, endophily (Betreten von Gebäuden) und synanthropy (Lebensgefährten mit dem Menschen) 2. .. Lebensmittelbedingte Krankheitserreger wie Salmonellen, Listeria monocytogenes, Campylobacter spp, Escherichia coli O157: H7, und Mitglieder der Gattung Cronobacter (Enterobacter sakazakii früher) wurde berichtet, dass durch Insekten 3-5 übertragen werden. Kulturfolger Dreck fliegt mechanisch durch Lebensmittel übertragenen Bakterien durch die Übertragung von Krankheitserregern von ihren Kontaminierte Hautflächen zu verbreiten. Jedoch kann das Vorhandensein von Krankheitserregern im Verdauungstrakt von Fliegen bis zu drei Mal seingrößer ist als die auf ihren Körperoberflächen (Körper, Kopf, Beine und Flügel) 5 beobachtet. Lebensmittelvergiftung Pathogene können auch Verdauungskanal der Fliege bleiben für eine größere Länge der Zeit, als auf der Körperoberfläche 6,7 und in einigen Fällen sind sie in der Lage, sich zu vermehren, besiedeln Verdauungstrakt 4,8,9 der Fliege. Dadurch erhöht sich das Vektorpotential von Fliegen, weil sie weitere Lebensmittelvergiftung Pathogene zu verbreiten durch Stuhlgang und Aufstoßen 10,11.
Heutzutage gibt es eine verbesserte Überwachungssysteme, die in der Lage, Lebensmittelvergiftungen Ausbrüche schneller zu erkennen sind. Bei der Durchführung von lebensmittelbedingten Krankheitsausbrüchen, die öffentliche Gesundheit Beamten suchen nach dem Essen, dass die Quelle (n) oder Fahrzeug (e) der Infektion sein kann. Die Ermittler können auch eine Umweltprüfung der Anlage (oder Anlagen) beteiligt, um herauszufinden, wie die Lebensmittel kontaminiert wurde durchgeführt und können Proben im Rahmen der Untersuchung 12 zu sammeln. Despite die große Menge an wissenschaftlicher Literatur über die Insekten als Träger von Krankheitserregern, die Verknüpfung von Insekten als Vektoren der Erreger eine bestimmte Lebensmittelvergiftung Ausbruch war eine Herausforderung. Dies ist vor allem, weil Insekten werden nicht aseptisch als Teil der Umweltprobenentnahmen während der lebensmittelbedingten Krankheitsausbrüchen gesammelt. Um Insekten, insbesondere solche, die Verhaltensweisen, die die Verbreitung von Krankheitserregern begünstigen aufweisen, im Rahmen einer Umweltprobenverfahren, eine standardisierte, schnelle, empfindliche und zuverlässige Protokoll, um Lebensmittelvergiftung Pathogene erkennen aus einem einzigen Insekten muss vorhanden sein, umfassen.
Traditionelle Plattierungstechniken zum Nachweis von Krankheitserregern von Insekten sind mühsam und hängen von der Wettbewerbs Wachstum der Zielbakterien in verschiedenen Kulturmedien, um das schnelle Wachstum des angeborenen kommensale Mikrobiota des Insekts zu überwinden. Die meisten Studien, die Insekten mit ba verbunden habencterial Krankheitserreger haben die Empfindlichkeit der Methode durch Bündelung mehrerer Insekten anstatt Identifizierung der Anwesenheit von Krankheitserregern auf einer pro Einzelfall erhöht. So haben diese Studien nicht den Körper ein Teil der Insekten, wo die Erreger gefunden 13-18 unterscheiden. Die Fähigkeit zu erkennen, ob Lebensmittelvergiftung Pathogene sind auf der Körperoberfläche oder im Verdauungstrakt eines einzelnen Insekten gelegen ist wichtig, da dies epidemiologische Auswirkungen haben und können zu unterschiedlichen Minderungsstrategien führen. Als mechanische Vektoren, Fliegen, dass Flächen für Nahrungsmittel für eine kurze Zeit nur geringe Mengen an Bakterien übertragen von ihrer Körperoberfläche, wohingegen jene Fliegen, erbrechen und verrichten auf der Nahrung erhöhen die Wahrscheinlichkeit der Übertragung von Krankheitserregern auf potenziell höhere Infektion. Folglich ist es wichtig, die Häufigkeit einer foodborne pathogen schätzen pro einem einzelnen Insekten und den Körperteil von diesem Insekt mit einer Keim p differen athogen befindet.
Auch wenn die Verwendung von kulturunabhängige Verfahren zur Lebensmittelvergiftung Pathogene erkennen zunehmend umgesetzt, haben sie nicht kommerziell verwendet werden, um Lebensmittelvergiftung Pathogene aus einer Insekten erkennen. Derzeit gibt validiert molekulare Protokolle, die im Handel für den schnellen Nachweis von Krankheitserregern von Lebensmitteln, die von der Industrie und Regulierungsbehörden verwendet werden, zur Verfügung stehen. Diese Verfahren umfassen DNA-basierende Systeme zum Nachweis von Pathogenen in einer Vielzahl von Lebensmittelproben. Obwohl molekulare Protokolle sind schneller als herkömmliche Beschichtungsverfahren wird die Anreicherung der Probe erforderlich, um die Empfindlichkeit von 10 2 koloniebildenden Einheiten (CFU) des bakteriellen Pathogens in der Polymerasekettenreaktion (PCR), die benötigt -basierten Verfahren 19 erhalten. Zusätzlich wird Isolierung reiner Bakterienkolonien von PCR-positiven Proben benötigt, um die Krankheitserreger mit einschlägigen Methoden zu bestätigen.
content "> Ziel dieses Protokolls besteht darin, einen im Handel erhältlichen PCR-basierten System verwendet werden, um Krankheitserreger aus Nahrungsmitteln und Umweltproben zum Nachweis von Lebensmittelbakterien aus der Körperoberfläche und den Verdauungskanal eines einzelnen fly zu erfassen und weiter zu isolieren diejenigen standardisieren Erreger der samples.The Empfindlichkeit des hier beschriebenen Protokoll wurde zuerst mit Labor aufgezogen erwachsene Stubenfliegen (Musca domestica), die experimentell mit seriellen Verdünnungen von jeder bakteriellen Erreger gefüttert wurden kalibriert. Das standardisierte Protokoll wurde anschließend zur Erhebung 100 Wildfängen fliegt auf das Vorhandensein von Krankheitserregern von ihren Körperoberflächen und / oder Verdauungs Kanäle. Dies wird standardisiertes Protokoll ermöglicht den Gesundheitslabors auf Gesundheitsgefahren durch Insekten gestellt zu erkennen, so dass die Möglichkeit der Erhebung sie als Teil der Umweltprobenprogramm bei der Durchführung von Lebensmittelvergiftungen Ausbruchsuntersuchungen.Protocol
1. Erhebung von Fliegen
- Sammeln einzelnen Fliegen mit sterilen entomologischen Sweep Netze. Legen Sie die Netze in einem Kühler und übergeben sie an das Labor.
2. Dissection of Flies
- Immobilisieren keimfreien Bedingungen entnommen Fliegen, indem man sie bei -20 ° C für 5-7 min.
- Mit einer sterilen Pinzette Ort eine Fliege in einem sterilen 2 ml Röhrchen mit 1 ml vorgewärmten (37 ° C) gepuffertes Peptonwasser (BPW). Mischen Sie den Schlauch vorsichtig durch Kippen für 2 min. Es ist wichtig, dass der gesamte Körper der Fliege in Kontakt mit den Medien, so daß die an der Körperoberfläche (S) des Flug vorliegenden Mikrobioten wird dem BPW (BPW-S) übertragen werden. Das Röhrchen mit einer Nummer und Körperteil des fly (dh 1S).
HINWEIS: siehe Tabelle der spezifischen Reagenzien / Ausrüstung für eine detaillierte Beschreibung von Materialien und Reagenzien in diesem Protokoll erwähnt. - Mit einer sterilen Pinzette entfernen Sie die Fliege von den BPW-S Medien und Transferes auf eine leere und saubere 2-ml-Tube an die Oberfläche zu desinfizieren die Fliege. Das Teströhrchen, enthaltend die BPW-S Medien bei 37 ° C während der Durchführung der Desinfektion und Dissektion Protokoll.
- Oberflächen desinfizieren fly von in 1 ml 70% Ethanol für 1 Minute, gefolgt von einem Spülen mit sterilem destilliertem Wasser vor dem in 1 ml frisch hergestelltem 0,05% (v / v) Bleichlösung tauchen eintaucht. Spülen 3 mal mit sterilem destilliertem Wasser. Bringen Sie Wasser aus dem letzten Spülgang zu einem Autoklaven 2-ml-Tube.
HINWEIS: Entfernen Sie die Flüssigkeit jedes Mal mit Hilfe eines 1000 ul Mikropipette oder durch Umdrehen des Röhrchens, um sicherzustellen, die Fliege in der Röhre bleibt. Vorsichtig mischen durch Umdrehen bei jedem Schritt der Oberflächendesinfektionsprozess. - Um die Wirksamkeit des Desinfektionsprozesses zu bewerten, dann 100 & mgr; l des Wassers vom letzten Spülgang zu einer Trypticase-Soja-Agar (TSA) und Platte verteilt mit einer sterilen L-förmigen Einwegfass. Inkubieren Sie die Platte bei 37 ° C für 24 Stunden. Nach dem incubation, registrieren Sie das Vorhandensein von Bakterienkolonien.
HINWEIS: Die Anwesenheit von Bakterienkolonien auf der TSA-Platten zeigt eine ineffiziente Oberflächendesinfektionsprozess. Wenn dies eintritt, ist die Anwesenheit von Krankheitserregern nur auf der Körperoberfläche des Fliegen gemeldet werden, da Kreuzkontamination zwischen der Körperoberfläche und den Verdauungskanal kann nicht ausgeschlossen werden.
- Oberflächen desinfizieren fly von in 1 ml 70% Ethanol für 1 Minute, gefolgt von einem Spülen mit sterilem destilliertem Wasser vor dem in 1 ml frisch hergestelltem 0,05% (v / v) Bleichlösung tauchen eintaucht. Spülen 3 mal mit sterilem destilliertem Wasser. Bringen Sie Wasser aus dem letzten Spülgang zu einem Autoklaven 2-ml-Tube.
- Nach oberflächen Desinfektion der Fliege, dann in einem Stück autoklaviertem Papiertuch, um überschüssige Wasser und dann in eine sterile 60 mm Einweg-Petrischale entfernen.
- Legen Sie die Petrischale unter einem Binokular und Identifizierung der Fliege auf Artenebene mit dichotomen Schlüssel für dipteran Familien 20,21.
- Mit autoklaviert feine Spitze Pinzette vorsichtig den Anus und den ganzen Verdauungskanal (A) aus dem Fliegen und aseptisch an einen anderen sterilen 2 ml Röhrchen mit 1 ml vorgewärmten (37 ° C) BPW mit 0,5 mm Zirkonia / Kieselsäure Perlen (BPW-A). Label-the Rohr mit der gleichen Anzahl für den einzelnen Fliegen und dem Körperteil der Fliege (dh 1A) ausgewählt.
- Mischen Sie die Röhrchen mit dem BPW-A gründlich für 5 bis 10 Minuten unter Verwendung einer Zelle Disruptor. Inkubiere bei 36 ± 1 ° C während der Durchführung der Rest des Protokolls.
- Um Voucher und / oder speichern Sie die Probe für die langfristige, setzen Sie den Rest der Fliege in ein sauberes 2-ml-Röhrchen und fügen Sie 1-2 ml 95% Ethanol.
3. Primäre und sekundäre Anreicherung
- Beschriftet alle primären und sekundären Anreicherung Röhrchen Medien nach der Probennummer und dem Körperteil der Fliege.
- Unter einer sterilen Haube, Transfer 300 ul BPW-S (Oberfläche) bis 2-ml-Röhrchen mit folgenden Medien steril:
- Salmonella, verwenden Sie 1 ml vorgewärmten (42 ° C) BPW. Inkubation in einem umlaufenden Wasserbad bei 42,5 ° C für 22 bis 24 h. Für sekundäre Anreicherung, dann 100 & mgr; l von angereichertem BPW auf 400 & #181; l vorgewärmtes (37 ° C) Gehirn-Herz-Infusions (BHI) -Brühe zuvor steril Cluster-Röhrchen gegeben. Bei 37 ° C für 3 Stunden.
- Für Cronobacter Verwenden 1 ml vorgewärmtes (37 ° C) BPW mit Novobiocin (10 mg / L; Wallace, M., persönliche Mitteilung). Alternativ können Sie 1 ml der R & F Enterobacter sakazakii Anreicherungsbouillon mit Aufpreis (Vancomycin und Cefsulodin) als primäre Bereicherung. Bei 37 ° C für 22 bis 26 h. Für sekundäre Anreicherung, dann 100 & mgr; l von angereichertem BPW mit Novobiocin zu 400 ul vorgewärmten (37 ° C) BHI-Bouillon zuvor in sterile Cluster-Röhrchen gegeben. Bei 37 ° C für 3 Stunden.
- Für L. monocytogenes, verwenden Sie 1 ml frisch zubereitet RT 24 Listeria-Anreicherungsbouillon (24 LEB) mit Selektiv-Supplement. Bei 37 ° C für 44 ± 5 Stunden. Die sekundären Anreicherung für den Nachweis von L. erforderliche monocytogenes. Wiederholen Sie die Schritte 3.2.1 - 3.2.3 mit dem Rohr als BPW-A bezeichnet.
4. Herstellung des PCR-basiertes System für die Amplifikation und Detektion der Zielborne Pathogen
Die Schritte 4-8 mit einem kommerziellen PCR-Cycler / Detektor-System, ein Computerarbeitsplatz und ready-to-use-Kits für Salmonellen (Salmonella 2 Standard-Assay-Kit), Cronobacter Arten (E. sakazakii Standard-Assay-Kit) und Listeria monocytogenes Bildschirm (L. monocytogenes-24E-Assay-Kit). Standardtests verwenden PCR Endpunktbestimmung. Jeder Satz enthält PCR-ready-Tabletten mit einem interkalierenden Farbstoff, der ein Fluoreszenzsignal bei Bindung an doppelsträngige DNA aussendet. Das Signal wird während der Erkennungsphase des PCR-System-Programm erfasst, Erzeugen einer Schmelzkurve, die von der Software als positiv oder negativ bewertet wird.
- Bereiten Sie Reagenzien und Geräte wie die manufactu angegebenrer Protokoll für jede Ziellebensmittelbedingten Krankheitserreger.
HINWEIS: Die Protokolle zum Nachweis von Salmonellen und Cronobacter erfordern eine Ein-Schritt-Lyseverfahren Das Protokoll zum Erfassen L. monocytogenes ist eine Zwei-Schritt-Lyseverfahren (siehe Abschnitte 5 bzw. 6). - Schalten Sie den automatisierten Heizblock Auswahl des spezifischen Programms für Zielpathogens. Alternativ, wenn die Thermoblöcke sind manuell, eingestellt Temperaturen bis 37 ° C (für Salmonellen, Cronobacter spp und Listeria monocytogenes.) Oder auf 55 ± 2 ° C (für L. monocytogenes Teil 2 der Lyse - siehe Schritt 6.2) und 95 ± 3 ° C.
- Stellen Sie sicher, dass die Kühlblöcke wurden gekühlt O / N, sonst entspannen sie bei 2 - 8 ° C für mindestens 2 Stunden.
- Mit der Computer-Software des PCR-basierten Detektionssystems, erstellen Sie eine Rack-Datei nach den Anweisungen des Herstellers.
- Beschriften und ordnen ClusterRöhrchen mit dem Lysereagenz in dem Gestell, entsprechend dem Gestell Datei.
- Initialisieren Sie die PCR-basierten Detektionssystems Instruments.
5. Führen Sie Lyse zum Nachweis von Salmonellen und Cronobacter
- Bereiten Sie das Lyse-Reagenz durch Zugabe von 150 ul Protease auf eine 12 ml Flasche Lysepuffer.
- Übertragen 200 ul Lysereagens zu jeder der zuvor markierte Cluster Röhren.
HINWEIS: - 8 ° C für bis zu 2 Wochen Cluster Röhrchen mit dem Lysis-Reagens kann in 2 gespeichert. - Mit langPipettenSpitzen, Transfer 20 ul sekundären angereicherte Proben (siehe Schritte 3.2.1 und 3.2.2) mit den entsprechenden Cluster Röhrchen mit 200 ul Lyse-Reagenz. Verwenden Sie neue Pipettenspitzen für jede Probe.
HINWEIS: Bewahren Sie Rohre aus primären und sekundären Anreicherung im Kühlschrank (Salmonellen) oder bei Raumtemperatur (Cronobacter) für eine weitere Bestätigung Analyse von PCR-positive / negative Proben. Bereiten Negativkontrollen durch Zugabe von 20 ul sterilem BHI Medium Cluster Röhrchen 200 ul Lysereagens. - Die Positivkontrollen durch Zugabe von 20 ul O / N Bakterienkulturen (in BHI) von jeder bekannten Salmonellen oder Cronobacter Stamm Cluster Röhrchen mit 200 ul Lyse-Reagenz.
- Cap-Cluster Rohre und sichern Sie fest mit dem Capping Werkzeug.
- Legen Sie das Rack von Cluster-Röhren in der automatisierten Heizblock nach Auswahl des spezifischen Programms für Zielpathogens. Alternativ inkubieren Cluster-Röhrchen bei 37 ± 2 ° C für 20 min, gefolgt von einer Inkubation bei 95 ± 3 ° C für 10 min. Schließlich übertragen die Cluster Rohre Kühlblöcken (2 - 8 ° C) für 5 min.
HINWEIS: Cluster Röhrchen mit dem Lysat bei -20 ° C für bis zu 2 Wochen gelagert werden.
6. Führen Lyse zum Nachweis von L. monocytogenes
- Führen Sie Teil einer derLyse, wie folgt:
- Fügen Sie 1,8 ml sterilem entionisiertem Wasser auf die Flasche vollständig aufgetaut Lysemittel 1.
HINWEIS: Shop Lysemittel 1 bei 2 - 8 ° C bis zum Gebrauch. Nach dem Öffnen und Verdünnen, Lagerung bei Raumtemperatur (20-30 ° C) für bis zu 6 Monaten. - Kombinieren Lysemittel 1 und 2 in einem Verhältnis 4: 1 (40 & mgr; l verdünnt Lysemittel 1 und 10 & mgr; l Lysemittel 2 pro jede Probe). Dann werden 50 ul der vereinigten Lysemittel Rohre clustern. Verwenden Sie die Mischung innerhalb von 4 Std.
- Gib 500 ul primäre angereicherten Probe (siehe Schritt 3.2.3) zum Cluster Röhrchen mit den 50 & mgr; l der vereinigten Lysemittel.
- Vorbereiten einer negativen Kontrolle durch Zugabe von 500 ul sterilem 24 LEB bis 50 & mgr; l der vereinigten Lysemittel.
- Bereiten Sie eine positive Kontrolle durch Zugabe von 500 ul O / N L. monocytogenes-Kultur in 24 LEB zu 50 & mgr; l der vereinigten Lysemittel gezüchtet.
- Verschließen Sie die Cluster-Röhrchen, vorsichtig mischen und Ortim Heizblock bei 37 ± 1 ° C für 30 min.
HINWEIS: Halten Sie Rohre von der Grundanreicherung in den Kühlschrank für eine weitere Bestätigung Analyse von PCR-positive / negative Proben.
- Fügen Sie 1,8 ml sterilem entionisiertem Wasser auf die Flasche vollständig aufgetaut Lysemittel 1.
- Führen Sie Teil 2 der Lyse, wie folgt:
- Bereiten Sie das Lyse-Reagenz wie in den Schritten 5.1 und 5.2 unterrichtet.
- Mit langPipettenSpitzen über 20 ul Teil eines Lysats auf Cluster-Röhrchen mit 200 ul Lyse-Reagenz. Verwenden Sie neue Pipettenspitzen für jede Probe.
- Cap-Cluster Rohre und sichern Sie fest mit dem Capping Werkzeug.
- Platz Cluster Rohre in automatisierten Heizblock Auswahl des spezifischen Programms für L. monocytogenes. Alternativ inkubieren Cluster-Röhrchen bei 55 ± 2 ° C für 30 min, gefolgt von einer Inkubation bei 95 ± 3 ° C für 10 min. Schließlich übertragen die Cluster Rohre Kühlblöcken (2 - 8 ° C) für 5 min.
HINWEIS: Cluster Röhrchen mit dem Lysat bei -20 ° C für bis zu 2 Wochen gelagert werden.
7. Hydrate PCR-Ready Tabletten
- Wählen Sie ein gekühlt (4 ° C) PCR-Kühlblock und setzen Sie ein PCR-Röhrchen-Rack über den Einsatz.
- Zeigen entsprechenden PCR-Röhrchen mit der PCR-ready Tabletten (mit jedem Kit enthalten) für die Ziellebensmittelbedingten Krankheitserreger in die Halterung nach der Rack-Datei.
- Mit der Entdeckelungsvorrichtung, entfernen Sie vorsichtig die Kappen von PCR-Röhrchen. Entsorgen Sie die Kappen und überprüfen, dass jedes Rohr enthält eine Tablette.
- Transfer 50 ul (auf Salmonellen und Cronobacter) oder 30 ul (für L. monocytogenes) des Lysats auf spezifische PCR-Röhrchen. Verwenden Sie neue optische Kappen und dicht zu befestigen auf die PCR-Röhrchen mit dem Capping Werkzeug.
HINWEIS: Nach der Zugabe des Lysats auf PCR-ready Tabletten, Proben müssen bei 2 gekühlt bleiben - 8 ° C bis in den PCR-basierten Nachweissystem geladen. Die PCR-Röhrchen können bei 2.500 xg für einige Sekunden zentrifugiert, um sicherzustellen, daß das gesamte Volumen in der unteren t werdener Rohr. - Laden Sie die PCR-Röhrchen in die PCR-Cycler / Detektionssystem Instrument durch Öffnen des Gerätes Schublade.
- Legen Sie das Rack von PCR-Röhrchen in die Vertiefungen in der Schublade und prüfen Sie, dass die Rohre richtig sitzt.
- Schließen Sie die Schublade und leitet das Programm von dem Protokoll des Herstellers beschrieben.
HINWEIS: Die PCR-basierte Instrument Radfahren Parameter für jeden lebensmittelbedingten Krankheitserreger voreingestellt. - Stellen Sie sicher, dass die PCR-Zyklusstatusleiste zeigt ein blauer Balken anzeigt, dass der Verstärkungsteil des Programms läuft.
HINWEIS: Für Standard-PCR-Assays, die Verarbeitungszeit des vollständigen Programms (Amplifikation und Detektion) dauert etwa 3-3,5 Stunden in Anspruch.
8. Überprüfen Ergebnisse
- Nach der Bearbeitung ist, befolgen Sie die Bildschirmanweisungen aus der PCR-basierten System Instrument, um Proben und als Ergebnis hieraus zu entfernen.
- Wenn die Zielfoodborne pathogen ist in der Probe vorhanden ist (entweder dasOberfläche oder der Verdauungskanal der Fliege) der Brunnen ist rot mit einem "Plus" Vorzeichen (positiv). Wenn der Erreger nicht vorhanden ist, ist das auch grün mit einem Minuszeichen (negativ).
- Wenn das gut ist gelb mit einem roten Balken in der Mitte, gibt es einen Signalfehler.
9. Isolierung von bakteriellen Erregern von PCR-positive Ergebnisse
- Wählen Sie die Rohre von der primären (für L. monocytogenes) oder sekundären (auf Salmonellen und Cronobacter) Anreicherung von den Proben, die PCR-positiv waren. Auch nach dem Zufallsprinzip wählen Sie 3-5% der Proben, die PCR-negativ waren, und gehen Sie folgendermaßen vor:
- Für Salmonellen:
- Füge 100 & mgr; l des sekundären Anreicherungsmedien auf 10 ml Rappaport-Vassiliadis (RV) Medium und 1 ml Tetrathionat (TT) Brühe. Rohre mit 42,5 ° C inkubieren in einer Umlauf Wasserbad für 22-24 Stunden.
- Nach der Inkubation Streifen a 3 mm Öse (10 ul) von jedem, RV eind TT Medien auf Bismut-Sulfit (BS) Agar Xylose-Lysin-Desoxycholat (XLD) Agar und Hektoen-Entero (HE) Agar. Platten bei 35 ± 1 ° C für 22 bis 24 h.
- Nach der Inkubation untersuchen Platten auf die Anwesenheit von typischen Salmonellenkolonien auf jedes Medium. Wenn keine isolierten Kolonien können nach mehreren Unter Kultivierung Schritte erhalten werden, sollten Sie die Probe als negativ und berichten als falsch positiv für die PCR-basierten System.
HINWEIS: Für typische Salmonellen Kolonien auf bestimmten Medien sehen 22. Wählen fünf mutmaßlichen typischen Salmonellenkolonien und Subkultur sie auf BS, XLD oder HE bis Reinkulturen isoliert / einzelne Kolonien erhalten werden. - Wählen Sie einen reinen Kolonie und identifizieren mutmaßlichen Salmonellen mit Hilfe biochemischer kommerziellen Tests wie der VITEK 2 Personalausweis oder API biochemischen Erkennungssystem, nach den Anweisungen des Herstellers.
- Für Cronobacter: <ol>
- Streak ein 3 mm Öse (10 ul) der Sekundäranreicherungsmedien auf zwei Platten aus chromogene Medien wie R & F Enterobacter sakazakii (Cronobacter) chromogene Beschichtungsmediums und / oder chromID Sakazakii Agar. Platten bei 35 ° C für 22 bis 24 h.
- Nach der Inkubation untersuchen Platten auf das Vorhandensein von typischen Cronobacter Kolonien (blau-schwarz zu blau-grau). Wählen Sie 5 mutmaßlichen Cronobacter Kolonien und Subkultur sie auf R & F Enterobacter sakazakii (Cronobacter) chromogenen Plattierungsmedium, chromID Sakazakii Agar oder TSA, bis Reinkulturen isoliert / einzelne Kolonien erhalten werden.
HINWEIS: Wenn keine isolierten Kolonien können nach mehreren Unter Kultivierung Schritte erhalten werden, sollten Sie die Probe als negativ und berichten als falsch positiv für die PCR-basierten Detektionssystems. - Wählen Sie einen reinen Kolonie und identifizieren mutmaßlichen Cronobacter mit Hilfe biochemischer handelszielle Tests wie der VITEK 2 Ausweis oder API 20E biochemische Identifikationssystem nach den Anweisungen des Herstellers.
- Streak ein 3 mm Öse (10 ul) der primären Anreicherungsmedien auf zwei Platten der Brillanz Listeria-Agar (BLA). Platten bei 36 ± 1 ° C für 22 bis 26 h.
- Nach der Inkubation untersuchen Platten auf die Anwesenheit von L. präsumtive monocytogenes (blaugrün) Kolonien. Wählen Sie 5 mutmaßlichen L. monocytogenes Kolonien und Subkultur sie auf BLA bis man Reinkulturen isoliert / Einzelkolonien. Wieder inkubieren negativen Platten bei 36 ± 1 ° C für weitere 22 bis 26 Std.
- Wählen Sie einen reinen Kolonie und identifizieren mutmaßlichen L. monocytogenes unter Verwendung gewerblicher biochemische Tests wie dem VITEK 2 Personalausweis oder API Listeria biochemische Identifikationssystem, nach Angaben des Herstellers inweise.
Representative Results
C. - Dieses Protokoll wurde zuerst auf einer Reihe von Labor aufgezogenen Hausfliegen, die experimentell für 24 h mit flüssigem Fliegenfutter (2% Milchpulver) mit seriellen Verdünnungen (10 & sup8; CFU / ml 10 2) zugeführt wurden kalibriert sakazakii, S. enterica, L. monocytogenes oder C. jejuni (n = 21 für jeden bakteriellen Pathogens). Anreicherungsmedien sowie Inkubationszeiten und Temperaturen wurden für jede foodborne pathogen eingestellt, bis die PCR-basierte System war in der Lage, die niedrigsten Niveaus von Bakterien (10 2 CFU / ml) von der Körperoberfläche und den Verdauungskanal eines einzelnen experimentell speist detektieren fliegen. Mit den Anreicherungsmedien und Bedingungen der Protokoll beschrieben, ermittelt die PCR-basierte System C. sakazakii, S. ente und L. monocytogenes von der Körperoberfläche von 100% der Fliegen mit bakteriellen Inokula> 10 3 CFU / ml (1A) gespeist wird. Wenn Fliegen wurden mit 10 zugeführt2 CFU / ml, der Prozentsatz der Nachweis von C. sakazakii, S. ente und L. monocytogenes von ihrer Körperoberfläche war 100%, 66% und 33%, bzw. (1A). Der PCR-basierte System erfasst auch diese drei Krakheitserregern aus den Verdauungskanal von Fliegen mit allen Bakterienkonzentrationen Prozent ≥33% (1B) zugeführt. Jedoch ist die Detektion von C. jejuni wurde nur erreicht, wenn im Labor aufgezogene Fliegen wurden experimentell mit flüssigen Lebensmitteln, die den höchsten bakteriellen Inoculum (10 & sup8; CFU / ml) zugeführt. Daher C. jejuni wurde aus der Gruppe der durch Lebensmittel übertragenen Krankheitserreger, die von den einzelnen Kulturfolger Schmutzfliegen mit dieser PCR-basierten Detektionssystems getestet werden konnte ausgeschlossen.
Mit diesem standardisierten Protokoll, konnten wir die Prävalenz von Cronobacter spp., S. enterica und L. monocytogenes von der Körperoberfläche und / oder the Verdauungskanal von 100 wilden Fliegen, die einzeln und steril waren aus dem Papierkorb Fläche von zehn städtischen Restaurants in Großraum Washington, DC 5 Gesammelte Dreck fliegt Vertreter von mindestens sechs Arten, darunter M. waren sich gefangen domestica (47%), Lucilia cuprina (33%), L. sericata (14%), Cochliomyia macellaria (2%), Sarcophaga haemorrhoidalis (2%) und Ophyra leucostoma (1%). Eine Fliege wurde nur auf Familienebene identifiziert (Anthomyiidae; 1%). Die Oberflächendesinfektion Protokoll war wirksam zur Vermeidung einer Kreuzkontamination zwischen den Körperteilen der Fliegen weil kein Bakterienwachstum auf TSA-Platten für Wasser aus dem letzten Desinfektionsspülung der einzelnen Fliegen beobachtet. Somit könnte eine Unterscheidung zwischen auf der Körperteile jedes fly vorliegende Lebensmittel relevante Bakterien erfolgen.
Keine False Positives wurden aus Proben von Körperoberfläche und den Verdauungskanal erkannterEinzellinie bei der Verwendung dieser kommerziellen PCR-basiertes System für die Detektion von S. enterica und L. monocytogenes und die Bestätigung von lebensfähigen Erregern auf Agarplatten war in Übereinstimmung mit PCR-positiven Ergebnissen. War es jedoch nicht möglich, reine Kulturen von Cronobacter spp isolieren. von allen PCR-positiven Proben. Daher ist die Erkennung des Erregers durch die PCR-basierte System zeigte False Positives von der Körperoberfläche (50%; 9/18) und der Speiseröhre (48%; 16/33) einzelner freier Wildbahn gefangenen Fliegen. Zufällig ausgewählte PCR-negativen Proben, die auf bestimmten Medien ausplattiert wurden, bestätigte das Fehlen der lebensmittelbedingten Krankheitserregern. Daher wurden keine falsch-negative Ergebnisse aus einer der Proben bei der Verwendung dieser kommerziellen PCR-basierte System zu Cronobacter spp erkennen erkannt., S. ente oder L. monocytogenes.
Es werden nur die PCR-positiven Proben, bei denen der Erreger isoliert und bestätigt wurden als positivund für eine statistische Analyse eingeschlossen. Die Gesamt Vorhandensein von Krankheitserregern im Verdauungstrakt von wild gefangenen Dreck fliegt deutlich höher als auf der Körperoberfläche (χ 2 = 6,8772, df = 1, p = 0,0087). 22% der Nahrungs Kanälen und 8% der Körperoberfläche der gesammelten Wildfliegen waren positiv für mindestens einen der drei Krankheitserregern (Abbildung 2). Insgesamt hat sich die Prävalenz von Cronobacter spp. entweder auf den Körperoberflächen oder Verdauungs Kanäle gesammelten Fliegen war statistisch höher (19%; Fisher-Test p = 0,0165) als die Prävalenz von S. enterica (7%) und L. monocytogenes (4%). Es wurden jedoch keine statistisch signifikanten Unterschiede festgestellt, wenn die Durchführung paarweise Vergleiche zwischen den Körperteilen der Fliegen für jede bakterielle Erreger (3; Fisher-Test p = 0,1464, p = 0,1184 und p = 0,6212 für Cronobacterspp., S. ente und L. monocytogenes, respectively). Keine Fliegen waren positiv für alle drei Erreger untersucht. Jedoch drei der Fliegen (zwei L. cuprina und ein L. sericata) durchSalmonElla spp. und L. monocytogenes auf der Oberfläche oder in den Verdauungskanal.
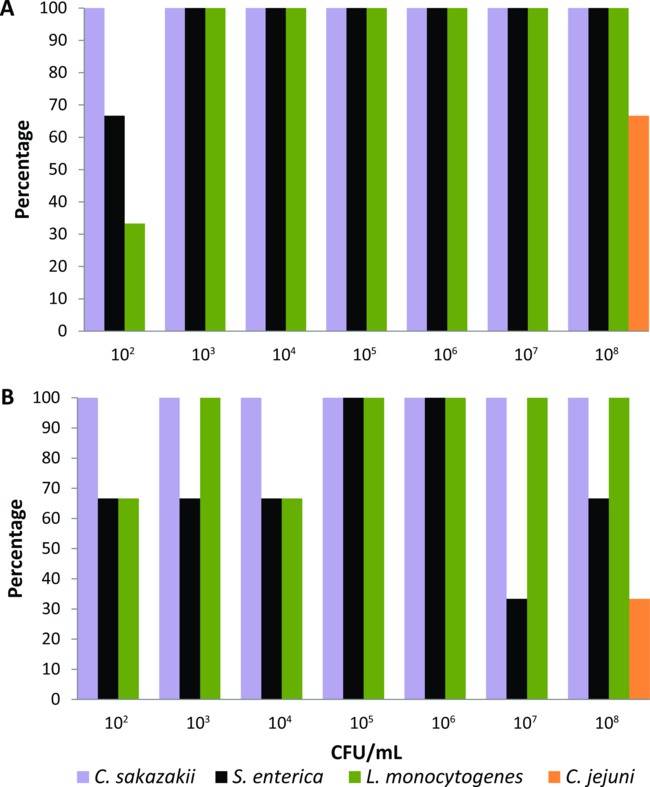
Abbildung 1. Erfassungsebenen von Cronobacter sakazakii, Salmonella enterica, Listeria monocytogenes und Campylobacter jejuni aus (A) der Körperoberfläche und (B) des Verdauungskanals der einzelnen Labor aufgezogen Stubenfliegen mit flüssigen Lebensmitteln mit verschiedenen bakteriellen Inokula zugeführt (n = 21 für jeden bakteriellen Pathogens, n = 3 für jede Bakterienkonzentration).
Abbildung 2. Prozentsatz der Körperoberflächen und Verdauungs Kanäle einzelner Fliegen positiv für eines der Zielkrankheitserregern.

Abbildung 3: Prävalenz von Cronobacter spp., Salmonella enterica und Listeria monocytogenes von der Körperoberfläche und der Verdauungstrakt des Kulturfolger wild gefangenen Fliegen. Die p-Werte angegeben sind von paarweisen Vergleiche zwischen der Körperoberfläche und den Verdauungskanal für jeden bakteriellen Erreger (Fisher-Test, p-Wert <0,05 zeigt statistische Signifikanz). Copyright © Amerikanischen Gesellschaft für Mikrobiologie, Journal of Applied and Environmental Microbiology 78 (22): 7891-902 2012 doi: 10,1128 / AEM.02195-12.
Discussion
Frühere Studien, die Lebensmittelvergiftung Pathogene aus wilden Insekten festgestellt haben, sind eine Vielzahl von Protokollen, die nicht darunter etwa die notwendigen Informationen, um genau beurteilen die ernährungsbedingten Risiken für die Anwesenheit eines einzigen Fliege in Lebensmitteln oder Lebensmittelbezogenen Umgebungen 13,15 verwendet, 23,24. Hier haben wir gezeigt, dass die Verwendung dieses standardisierten Protokoll ist es möglich, zu erfassen und zu isolieren Cronobacter spp., S. ente und L. monocytogenes von der Körperoberfläche und den Verdauungskanal der Einzelfliegen in freier Wildbahn gefangen. Da Insekten niedrigen Zahlen der Ziellebensmittelbedingten Krankheitserreger und eine hohe Zahl von anderen indigenen Mikroflora 25,26 zu tragen, dieses Protokoll primären (und manchmal sekundär) Anreicherung der Proben in spezifischen Kulturmedien, die Empfindlichkeit der Erfassung des Ziels durch Lebensmittel übertragenen Krankheitserreger zu erhöhen . Die Ergebnisse der PCR-basierten Nachweissystem wurden innerhalb von etwa 30 h erhalten (für die detektion von Cronobacter spp. und S. enterica) und 48 h (für den Nachweis von L. monocytogenes), nachdem zunächst die Bearbeitung der Proben. Somit ist dieses Protokoll zuverlässig sowie schnell und empfindlich genug, um Bildschirm eine Fliege auf das Vorhandensein von Krankheitserregern.
Bestätigung der PCR-positive Ergebnisse und die Isolierung von lebensfähigen Bakterien ist Teil des Standardverfahren von vielen Laboratorien. Darüber hinaus ist für Epidemiologie Zwecke reinen Bakterienkulturen von PCR-positiven Proben sind erforderlich, um weiter zu bestätigen und Serotyp der lebensmittelbedingten Krankheitserreger mit biochemischen, immunologischen oder genetischen Methoden. Obwohl keine False Positives beobachtet bei der Erkennung von S. enterica und L. monocytogenes aus den Körperteilen der einzelnen wild gefangenen Fliegen, die dieses Protokoll verwenden, fanden wir bis zu einer 50% Rate von False Positives für Cronobacter spp. Dies legt nahe, dass die PCR-basierten Nachweissystem für die Gattung Cronobacter kann zu Kreuzreaktionen mit anderen Enterobacteriaceae gehören zu den sehr komplexen Mikroflora durch Fliegen durchgeführten Ermittlungen zugegen. Somit Isolierung und Reinigung von reinem Kolonien der Gattung Cronobacter von PCR-positiven Proben erfordern selektives Plattieren als die anderen Pathogenen bewertet.
Dieses Protokoll wurde vor allem standardisiert worden, um einzelne wild gefangenen Fliegen auf das Vorhandensein von Cronobacter spp Bildschirm., S. ente und L. monocytogenes unter Verwendung eines kommerziellen PCR-basierten Nachweissystem. Jedoch wurde dieses Protokoll auch leicht angepasst werden, um Körperteile Einzellinie auf die Anwesenheit von anderen Krankheitserregern wie enterohämorrhagischen E. coli O157 screenen: H7 (entweder über den E. coli O157: H7 MP Standard-Assay-Kit oder die E. coli O157: H7 Echtzeit-Assay-Kit) und das Shiga-Toxin produzierenden E. coli (STEC) Gruppe (mit der Echtzeit-STEC suite), erhalten Empfindlichkeiten> 80% (unveröffentlichened-Daten). Außerdem kann dieses Protokoll möglicherweise angepasst werden, um Krankheitserregern aus anderen Insekten, die bekannte Vektoren von Krankheiten (Schaben und Ameisen) sind zu erkennen, aber die Forschung in diesem Bereich benötigt wird.
Lebensmittelvergiftungen Ausbruchsuntersuchungen sind sehr dynamisch und bestehen aus einem mehrstufigen Verfahren, die je nach der spezifischen Situation und die lokale Umgebung untersucht 12,27 variieren kann. Diese Untersuchungen sind wichtig, weil sie unmittelbaren Schutz der öffentlichen Gesundheit durch die Verhütung künftiger Erkrankungen bieten. Darüber hinaus können diese Untersuchungen neue Mechanismen, durch die Mikroorganismen in Lebensmitteln verteilt sind aufzuklären, und werfen wichtige Fragen, die neue Forschungsbereiche 28 führen. Ermittlungstechniken sowie standardisierte, schnelle und empfindliche Protokolle zum Nachweis von Krankheitserregern aus einzelnen Insekten notwendig. Diese standardisierten Protokolls eröffnet die Möglichkeit, aseptisch sammeln Insekten wie Fliegen, which können die lebensmittelbedingten bakteriellen Erreger Vektor, im Rahmen einer Umweltprobenprogramm. Die epidemiologischen Informationen, die daraus gewonnen werden können wäre der Verwendung bei der Konstruktion ein genaues Bild über die Mechanismen der Übertragung von Krankheitserregern durch Insekten (dh Länge der Belichtungszeit: eine Fliege von der Landung gegen Fliegen landen, Stuhlgang, und erbrechend).
Schließlich, obwohl die kommerzielle hier beschriebenen PCR-basierten Nachweissystem ist praktisch zu verwenden und vereinfacht die PCR-Amplifikation und Visualisierung eines Gattungsebene Amplikon, ist es keineswegs die einzige geeignete System. Das Lysat aus angereicherten Proben könnten alternativ verwendet werden, um auf das Vorhandensein von Krankheitserregern Bildschirm mit öffentlich verfügbaren artspezifischen Primer-Paare werden. Jedoch sollte die Nachweisempfindlichkeit vor ihrer Verwendung gezeigt werden.
Materials
| Name | Company | Catalog Number | Comments |
| Bismuth sulfite (BS) agar | Fisher Scientific | R452402 | *Multiple suppliers. |
| Brain heart infusion (BHI) broth | Becton, Dickson and Company | 299070 | *Pre-warmed to 37°C. Multiple suppliers. |
| Brilliance Listeria agar (BLA) | Fisher Scientific | CM1080B | *Multiple suppliers. |
| Buffered peptone water (BPW) | Becton, Dickson and Company | 212367 | *Pre-warmed to 37°C or 42°C. Multiple suppliers. |
| Brilliance Cronobacter agar (Druggan-Forsythe-Iversen formulation/DFI) | Fisher Scientific | CM1055B | *Multiple suppliers. |
| chromID Sakazakii Agar | bioMérieux | 43741 | *Call for information: 800.682.2666 |
| R & F Enterobacter sakazakii (Cronobacter) Chromogenic Plating Medium | R & F Laboratories | Various | *Call for information: +1.630.969.530 |
| R & F Enterobacter sakazakiii Enrichment Broth and supplement | R & F Laboratories | Various | *Call for information: +1.630.969.530 |
| Hektoen enteric (HE) agar | Fisher Scientific | OXCM0419B | *Multiple suppliers. |
| 24 Listeria enrichment broth (24LEB) | Oxoid | CM1107 | *Freshly prepared at room-temperature. Multiple suppliers. |
| Listeria selective enrichment supplement | Oxoid | SR0243 | *Multiple suppliers. |
| Novobiocin | Fisher Scientific | OXSR0181E | *Multiple suppliers. Store at 2-8 °C |
| Vancomycin hydrochloride hydrate | Sigma Aldrich | 861987 | Store at 2-8 °C |
| Cefsulodin sodium salt hydrate | Sigma Aldrich | C8145 | Store at 2-8 °C |
| Rappaport-Vassiliadis (RV) medium | Fisher Scientific | CM0669B | *Multiple suppliers. |
| Tetrathionate (TT) Broth | Becton, Dickson and Company | 249120 | *Multiple suppliers. |
| Trypticase soy agar (TSA) | Becton, Dickson and Company | 236930 | *Multiple suppliers. |
| Xylose lysine desoxycholate (XLD) agar | Becton, Dickson and Company | 221284 | *Multiple suppliers. |
| API Biochemical identification system | bioMérieux | Various | *Call for information: +1.800.682.2666 |
| VITEK 2: Product Safety | bioMérieux | Various | *Call for information: +1.800.682.2667 |
| BAX System Q7 | DuPont | ||
| BAX E. sakazakii Standard assay kit | DuPont | D11801836 | |
| BAX L. monocytogenes 24E assay kit | DuPont | D13608125 | |
| BAX Salmonella 2 Standard assay kit | DuPont | D14368501 | |
| Capping tool | DuPont | D11677028 | |
| Decapping tool | DuPont | D11134095 | |
| PCR tube rack/holder | DuPont | D12701663 | |
| Featherweight forceps, wide tip | BioQuip | 4750 | Sterilize before use. Multiple suppliers. |
| Fine point, straight tip forceps | BioQuip | 4731 | Sterilize before use. Multiple suppliers. |
| Zirconia/silica beads, 0.5 mm | Bio Spec Products, Inc. | 11079105z | Multiple suppliers. |
| Petri dishes - 60X15mm | Fisher Scientific | 08-772B | Multiple suppliers. |
| Disposable inoculating loops, 10µL | Fisher Scientific | 22-363-606 | Multiple suppliers. |
| L-shaped cell spreaders | Fisher Scientific | 14-665-230 | Multiple suppliers. |
| Microcentrifuge tubes, 2 ml | Fisher Scientific | Various | Sterilize before use when needed. Secure lid is preferred. Multiple suppliers. |
| Cluster tubes | Fisher Scientific | 05-500-13 | |
| Cluster tubes caps | Fisher Scientific | 05-500-23 | |
| Sodium hypochlorite (Liquid chlorine bleach) | *Dilute to 0.05% with water. Multiple suppliers. | ||
| Sterile deionized water | Multiple suppliers. | ||
| Sterile distilled water | Multiple suppliers. | ||
| Ethyl alcohol 190 proof | *Dilute to 70% with water when needed. Multiple suppliers. | ||
| Genie cell disruptor, 120V - for 1.5ml and 2.0ml microtubes | Scientific Industries, Inc. | SI-D238 | Multiple suppliers. |
| Heating block | Multiple suppliers. | ||
| Cooling block | Multiple suppliers. | ||
| Recirculating water bath | Multiple suppliers. | ||
| Stereo microscope | Multiple suppliers. | ||
| Centrifuge | Multiple suppliers. | ||
| Incubator | Multiple suppliers. |
References
- Voeller, J. G. Wiley Handbook of Science and Technology for Homeland Security. , Wiley Inc. 1-16 (2008).
- Olsen, A. R., Gecan, J. S., Ziobro, G. C., Bryce, J. R. Regulatory action criteria for filth and other extraneous materials V. Strategy for evaluating hazardous and nonhazardous filth. Regulatory Toxicology and Pharmacology. 33 (3), 363-392 (2001).
- Hald, B., Skovgård, H., Pedersen, K., Bunkenborg, H. Influxed insects as vectors for Campylobacter jejuni and Campylobacter coli in Danish broiler houses. Poultry Science. 87 (7), 1428-1434 (2008).
- Kobayashi, M., et al. Houseflies: Not simple mechanical vectors of enterohemorrhagic Escherichia coli O157:H7. American Journal of Tropical Medicine and Hygiene. 61 (4), 625-629 (1999).
- Pava-Ripoll, M., Pearson, R. E. G., Miller, A. K., Ziobro, G. C. Prevalence and relative risk of Cronobacter spp., Salmonella spp., and Listeria monocytogenes associated with the body surfaces and guts of individual filth flies. Applied and Environmental Microbiology. 78 (22), 7891-7902 (2012).
- Hewitt, C. G. Houseflies and how they spread disease. , Cambridge University Press. (1912).
- Rochon, K., Lysyk, T. J., Selinger, L. B. Retention of Escherichia coli by house fly and stable fly (Diptera:Muscidae) during pupal metamorphosis and eclosion. Journal of Medical Entomology. 42 (3), 397-403 (2005).
- Greenberg, B., Kowalski, J. A., Klowden, M. J. Factors affecting the transmission of Salmonella by flies: natural resistance to colonization and bacterial interference. Infection and Immunity. 2 (6), 800-809 (1970).
- Mramba, F., Broce, A. B., Zurek, L. Vector competence of stable flies, Stomoxys calcitrans L. (Diptera:Muscidae), for Enterobacter sakazakii. Journal of Vector Ecology. 32 (1), 134-139 (2007).
- Ekdahl, K., Normann, B., Andersson, Y. Could flies explain the elusive epidemiology of campylobacteriosis. Bmc Infectious Diseases. 5 (11), 11 (2005).
- Nayduch, D., Noblet, G. P., Stutzenberger, F. J. Vector potential of houseflies for the bacterium Aeromonas caviae. Medical and Veterinary Entomology. 16 (2), 193-198 (2002).
- Multistate and Nationwide Foodborne Outbreak Investigations: A Step-by-Step Guide. , CDC. Atlanta, GA. Available from: http://www.cdc.gov/foodsafety/outbreaks/investigating-outbreaks/investigations/index.html (2013).
- Sievert, K., Messler, S., Klimpel, S., Feffer, K. Comprehensive study on the occurrence and distribution of pathogenic microorganisms carried by synanthropic flies caught at different rural locations in Germany. Journal of Medical Entomology. 46 (5), 1164-1166 (2009).
- Hernández-Escareño, J. J., et al. Presence of Enterobacteriaceae, Listeria spp., Vibrio spp. and Staphylococcus spp. in house fly (Musca domestica L.), collected and macerated from different sites in contact with a few animals species. Revista Cientifica-Facultad De Ciencias Veterinarias. 22 (2), 128-134 (2012).
- Mian, L. S., Maag, H., Tacal, J. V. Isolation of Salmonella from muscoid flies at commercial animal establishments in San Bernardino county, California. Journal of Vector Ecology. 27 (1), 82-85 (2002).
- Olsen, A. R., Hammack, T. S. Isolation of Salmonella spp. from the housefly, Musca domestica L., and the dump fly, Hydrotaea aenescens (Wiedemann) (Diptera:Muscidae), at caged-layer houses. Journal of Food Protection. 63 (7), 958-960 (2000).
- Holt, P. S., Geden, C. J., Moore, R. W., Gast, R. K. Isolation of Salmonella enterica serovar Enteritidis from houseflies (Musca domestica) found in rooms containing Salmonella serovar Enteritidis-challenged hens. Applied and Environmental Microbiology. 73 (19), 6030-6035 (2007).
- Mramba, F., Broce, A., Zurek, L. Isolation of Enterobacter sakazakii from stable flies, Stomoxys calcitrans L. (Diptera:Muscidae). Journal of Food Protection. 69 (3), 671-673 (2006).
- Koyuncu, S., Andersson, M. G., Haggblom, P. Accuracy and Sensitivity of Commercial PCR-Based Methods for Detection of Salmonella enterica in Feed. Applied and Environmental Microbiology. 76 (9), 2815-2822 (2010).
- Gagné, R. Insect and mite pests in food, an illustrated. 1, U.S. Department of Agriculture and U.S. Department of Health and Human Service. 269-296 (1991).
- Greenberg, B. Flies and disease, Vol I. Ecology, classification and biotic associations. , Princeton University Press. (1971).
- Wallace, H. A., Jacobson, A., Hammack, T. S. Chapter 5 Salmonella. Bacteriological Analytical Manual. , Available from: http://www.fda.gov/downloads/Food/FoodScienceResearch/UCM244774.pdf (2007).
- Barro, N., Aly, S., Tidiane, O. C. A., Sababenedjo, T. A. Carriage of bacteria by proboscises, legs, and feces of two species of flies in street food vending sites in Ouagadougou, Burkina Faso. Journal of Food Protection. 69 (8), 2007-2010 (2006).
- Ugbogu, O. C., Nwachukwu, N. C., Ogbuagu, U. N. Isolation of Salmonella and Shigella species from house flies (Musca domestica L.) in Uturu, Nigeria. African Journal of Biotechnology. 5 (11), 1090-1091 (2006).
- Brownlie, J. C., Johnson, K. N. Symbiont-mediated protection in insect hosts. Trends in Microbiology. 17 (8), 348-354 (2009).
- Feldhaar, H. Bacterial symbionts as mediators of ecologically important traits of insect hosts. Ecological Entomology. 36 (5), 533-543 (2011).
- Foodborne disease outbreaks: Guidelines for investigation and control. , World Health Organization. Available from: http://www.who.int/foodsafety/publications/foodborne_disease/outbreak_guidelines.pdf (2008).
- Wright, A. P., Gould, L. H., Mahon, B., Sotir, M. J., Tauxe, R. V. Overview of the Impact of Epidemic-Assistance Investigations of Foodborne and Other Enteric Disease Outbreaks, 1946-2005. American Journal of Epidemiology. 174, S23-S35 (2011).



