박테리아 콜로니에서 군집 DNA 추출
English
Share
Overview
출처: 이안 페퍼 박사와 찰스 게르바 박사의 연구소 – 애리조나 대학교
데모 저자: 루이사 이크너
토양 내의 미생물 지역 사회에 대한 전통적인 분석 방법은 일반적으로 선택적 및 차동 매체 또는 직접 카운트 분석에 희석 및 도금 방법론을 활용하는 문화적 분석과 관련이 있습니다. 직접 카운트는 존재하는 박테리아의 총 수에 대한 정보를 제공하지만, 지역 사회 내에 존재하는 인구의 수 또는 다양성에 대한 정보를 제공하지 않습니다. 판 수는 총 문화 또는 선택 된 문화 인구의 열거를 허용하고, 따라서 존재하는 다른 인구에 대한 정보를 제공합니다. 그러나 토양 박테리아의 1% 미만이 쉽게 배율로 나오기 때문에 문화 정보는 그림의 한 조각만 제공합니다. 문화가 될 수 있는 공동체의 실제 분수는 문화적 수에 따라 선택된 매체에 따라 달라집니다. 단일 매체는 특정 매체에 가장 적합한 채우기를 선택합니다.
최근 몇 년 동안, 토양 샘플에서 추출 된 지역 사회 DNA를 연구의 장점이 명백해지고있다. 이 비문화 기반 접근 방식은 문화 기반 접근 방식보다 존재하는 실제 커뮤니티를 보다 더 대표하는 것으로 생각됩니다. 존재하는 인구의 모형에 관하여 정보를 제공하는 것 이외에, 이 접근은 또한 그들의 유전 잠재력에 관하여 정보를 제공할 수 있습니다. 다른 기술과 마찬가지로 DNA 추출로 얻을 수 있는 데이터에는 한계가 있습니다. 따라서 많은 연구자들은 현재 직접 및 문화적 수와 함께 DNA 추출을 사용하여 환경 샘플에서 얻은 데이터를 최대화합니다.
Principles
Procedure
Applications and Summary
Community DNA from cultured colonies or extracted from soil can be subjected to bioinformatics and “omic” approaches that allow for characterization of the original bacteria within the sample. The omic approaches include metagenomics – determination of “who” is within the community via 16S rRNA sequencing. This gives an estimate of the diversity within the community.
The number of bacterial cells in the original soil sample can also be calculated. Community DNA is extracted from a soil and quantified by spectroscopic analyses. The estimated quantity of DNA measured as µg DNA per mL of solution is related back to the total volume of DNA extracted in solution to give a total amount of DNA per g of soil. By knowing the theoretical value of DNA per cell, the total number of cells per g of soil can be calculated.
Example
A soil has 0.12 µg DNA per g of soil
If each cell has 4 fg of DNA
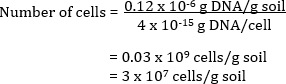
The extracted community DNA can be subjected to PCR analysis using specific primers to determine if a particular species is present within the community. Examples include specific bacterial pathogens such as Clostridium perfringens or Bacillus anthracis.
Transcript
Bacterial community DNA extraction is a process by which DNA is obtained from multiple bacterial species within a community during a single extraction procedure.
Traditional analyses of microbial communities in soil have usually involved cultural assays, utilizing dilution and plating methodology on different selective media. However, many bacteria grow poorly under laboratory conditions or on the specific growth media conditions selected, meaning they may be missed or severely underrepresented.
Recently, extracting community DNA from soil bacterial samples has allowed for a more comprehensive sampling of bacterial communities. This non-culture based approach is thought to be more representative of the actual communities present than traditional culture based methods.
This video will demonstrate a non-culture method of bacterial community DNA extraction, how to check the quality and quantity of extracted DNA, and explore how this DNA may be utilized to study bacterial diversity.
DNA extraction from soil can be conducted in one of two ways. In the fractionation method, cells are first separated from the soil matrix prior to extraction of the genetic material. The sample is then subjected to successive cycles of blending and slow centrifugation in order to collect intact cells in a pellet.
Lysozymes are then added to the cells, and the suspension is incubated. Lysozymes are enzymes that break down bacterial cell walls. Once the cell wall structure has been compromised, the DNA may then be liberated for purification. However, a second method of community DNA extraction, the in situ method, has been shown to yield greater DNA concentration.
Here, a mass of soil is combined with an equivalent volume of Tris-EDTA extraction buffer and glass beads, and mixed aggressively to facilitate separation of cells from the soil particles. A detergent is then added, generally sodium dodecyl sulfate, or SDS, and the sample is further blended to promote lysing of the cells and release of their contents, including DNA.
Incubation at a high temperature is then undertaken to lyse any remaining bacterial cells. Samples are centrifuged, and a polyethylene glycol extraction and incubation is performed on the supernatant in order to precipitate the DNA, which is then centrifuged into a pellet.
The DNA is resuspended in TE Buffer and potassium acetate in order to further wash the DNA of proteins and polysaccharides, then centrifugation is carried out to pellet these undesirable components. The aqueous supernatant containing the DNA is removed, and subjected to a phenol-chloroform extraction and isopropanol precipitation to further clean and concentrate the DNA. Following a room temperature incubation period of two hours, the DNA is centrifuged and resuspended in TE Buffer for storage until analysis.
Now that we are familiar with the concepts and processes behind bacterial community DNA extraction, let’s take a look at how it is carried out in the laboratory.
To begin the procedure, weigh out 100 g of sieved soil. Add this to a polypropylene vessel, and add 100 mL of extraction buffer comprised of Tris buffer amended with EDTA to promote the release of bacteria from the soil matrix, then shake by hand.
Next, weigh 100 g of glass beads, and add these to the mixing vessel. Agitate the sample for 5 min using a bead beating device or mechanical wrist-action shaker. Add 10 mL 20% sodium dodecyl sulfate, or SDS, to the mixture, then agitate for an additional minute. Incubate at a high temperature for 60 min.
Equally distribute the sample among separate 50 mL tubes, and centrifuge for 10 min at 6,000 x g. Transfer the supernatant from the tubes to a single sterile container. Next, repeat the extraction on the soil pellet as previously described, using a fresh volume of extraction buffer.
Next, add the total volume of processed supernatant to a clean 50-mL tube filled to half volume with a solution of 30% polyethylene glycol and 1.6 M sodium chloride. Invert the bottles several times by hand to mix, and incubate at room temperature for 2 h. Centrifuge samples at 10,000 x g for 20 min to pellet the DNA.
Remove the supernatant carefully from the centrifuge tube, leaving behind the partially purified nucleic acid pellet. Add 20 mL of TE Buffer and 1.5 mL of a 7.5 M potassium acetate solution to resuspend the pellet, then vortex. Place the suspension on ice for 5 min. Centrifuge at 16,000 x g for 30 min at 4 °C to precipitate proteins and polysaccharides.
Next, add an RNAse and proteinase K to the sample, mix gently by hand, and let sit for moment. Add an equivalent volume of phenol:chloroform:isoamyl alcohol to the suspension to be extracted, and mix gently by hand. Centrifuge the preparation for 10 min at 13,000 x g. Carefully remove the vessel from the centrifuge, and note the two layers.
The bottom, heavier layer is comprised of the phenol:chloroform:isoamyl alcohol and extracted debris, and the top layer is the aqueous and contains the DNA. Place the aqueous phase into a sterile vessel, add an equivalent volume of isopropanol, and invert gently to initiate DNA precipitation. Incubate the suspension at room temperature for 2 h. Pellet the purified DNA by centrifugation at 16,000 x g for 30 min. Carefully remove the supernatant as the pelleted DNA may or may not be visible at the bottom of the vessel, and then resuspend in 1 mL of TE Buffer.
Using a spectrophotometer or DNA/RNA quantification fluorimeter, measure the level of DNA extracted from the sample. DNA/RNA fluorimeters will output DNA levels in units of nanograms per milliliter. If the concentration is too high for accurate readings, dilute the suspension 1 to 10, or 1 to 100 using molecular grade water.
Once DNA is obtained from a bacterial community, this can be utilized in a number of different ways. Some of those applications are explored here.
Spectrophotographic analyses of the DNA extracted from community DNA can provide an insight into the number of bacterial cells present in a given soil sample. The estimated quantity of DNA in ng per mL of solution can be related back to the total volume of DNA extracted in solution, to give the total amount of DNA per g of soil. Knowing the theoretical value of DNA per cell, the total number of cells per g of soil can be calculated.
For more targeted applications, DNA extracted from bacterial communities can be subjected to PCR to determine if a particular species is present within the community. For example, scientists may want to identify whether soil samples contain specific pathogens, such as Clostridium perfringens or Bacillus anthracis.
Finally, to obtain a more comprehensive understanding of the bacteria present in a community, DNA samples can be subjected to “omic” and bioinformatic characterization that allow for deeper analysis of the original bacteria within the sample. “Omics” describes a range of technologies that explore roles, relationships, and actions of molecules in organisms or communities. This includes the studies of genes and their function, or “Genomics”, and “Proteomics”, the study of proteins and their roles. For example, sequencing of 16S RNA from the samples can allow a metagenomic determination of specific species within the community, giving a more detailed estimate of diversity. This approach can give scientists a better understanding of the species makeup of a community, and what roles they may be undertaking.
You’ve just watched JoVE’s introduction to bacterial community DNA extraction. You should now understand how to extract DNA from a bacterial community, how to check the quality of this DNA, and how this DNA can be used for investigations of bacterial community composition. Thanks for watching!
